Abstract
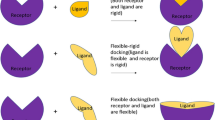
Two-dimensional (2D) well-accepted structure diagrams convey the elemental build-up of molecules, while three-dimensional (3D) presentations show the arrangement in space and the overall shape of molecules. However, much more information can be annotated graphically: New methods show protein-ligand complexes well-arranged in 2D, annotate scoring values of docking calculations or evaluations of 3D molecule conformations and extend the standard structure diagram depiction to complex chemical patterns.
Similar content being viewed by others
Literatur
Brecher J, Degtyarenko KN, Gottlieb H et al. (2008) Graphical representation standards for chemical structure diagrams. Pure Appl Chem 80:277–410
O’Donoghue SI, Goodsell DS, Frangakis AS et al. (2010) Visualization of macromolecular structures. Nat Methods 7:42–55
Schneider N, Lange G, Hindle S et al. (2013) A consistent description of HYdrogen bond and DEhydration energies in protein-ligand complexes: methods behind the HYDE scoring function. J Comput Aided Mol Des, doi: 10.1007/s10822-012-9626-2
Stierand K, Rarey M (2010) Drawing the PDB — proteinligand complexes in two dimensions. Med Chem Lett 1:540–545
Schärfer C, Schulz-Gasch T, Ehrlich H-C et al. (2013) Torsion angle preferences in drug-like chemical space: a comprehensive guide. J Med Chem, doi: 10.1021/jm3016816
Schomburg K, Ehrlich H-C, Stierand K et al. (2010) From structure diagrams to visual chemical patterns. J Chem Inf Model 50:1529–1535
Author information
Authors and Affiliations
Corresponding author
Additional information
Karen T. Schomburg 2004–2007 Biochemie — studium Bachelor of Science an der Ruhr-Universität Bochum. 2007–2009 Bioinformatikstudium Master of Science an der Universität Hamburg. Seit 2010 Promotion am Zentrum für Bio — informatik, Universität Hamburg.
Katrin Stierand 1998–2002 Medizinstudium an der Universität zu Köln und Universität Hamburg, 1. Staatsexamen. 2002–2005 Bioinformatikstudium an der Universität Hamburg, Diplom. 2005–2011 Promotion am Zentrum für Bioinformatik, Universität Hamburg. Seit 2012 Postdoc am Zentrum für Bioinformatik, Universität Hamburg.
Matthias Rarey 1988–1992 Informatikstudium an der Universität-GH Paderborn. 1993–1996 Promotion an der Universität Bonn. 1993–2002 wissenschaftlicher Mitarbeiter bei der GMD — Forschungszentrum Informationstechnik GmbH, Bonn, später Fraunhofer Institut für Algorithmen und Wissenschaftliches Rechnen SCAI, Sankt Augustin. 1997 und 2000 Forschungsaufenthalte bei SmithKline Beecham, Philadelphia und Roche Bioscience, Palo Alto, USA. Seit 2002 Professor an der Universität Hamburg, Direktor des Zentrums für Bioinformatik (ZBH).
Rights and permissions
About this article
Cite this article
Schomburg, K.T., Stierand, K. & Rarey, M. Visualisierung komplexer, molekularer Zusammenhänge. Biospektrum 19, 146–148 (2013). https://doi.org/10.1007/s12268-013-0285-1
Published:
Issue Date:
DOI: https://doi.org/10.1007/s12268-013-0285-1